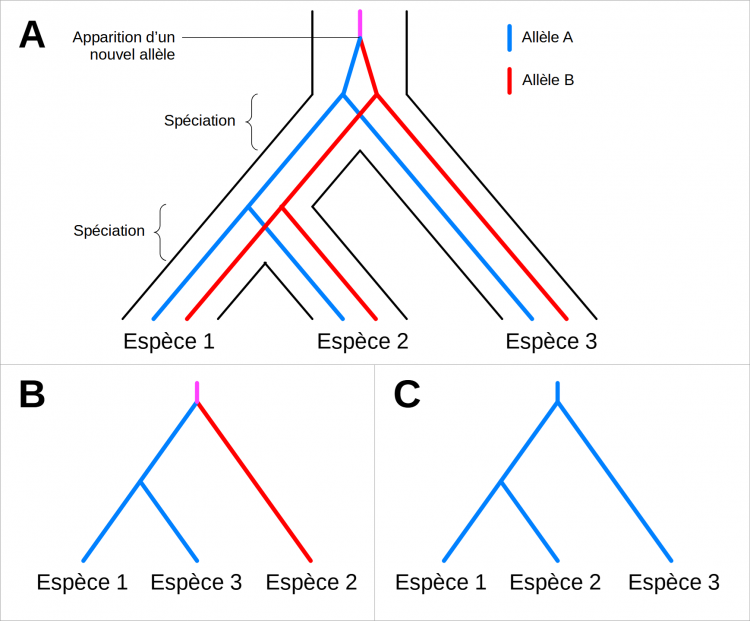
A. Histoire phylogénétique réelle d’une lignée montrant les évènements de spéciation et de diversification génétique avec l’exemple des allèles A et B issus d’un même allèle ancestral. Les allèles A et B sont deux versions d’un même gène qui coexistent chez les trois espèces.
B. Arbre phylogénétique des espèces biaisé, construit avec les séquences des allèles A des espèces 1 et 3, et la séquence de l’allèle B de l’espèce 2. Les allèles A et B sont paralogues.
C. Arbre phylogénétique des espèces non biaisé, construit avec les séquences des allèles A des trois espèces. Les différentes versions de l’allèle A sont orthologues.
Le biais de la paralogie dans la reconstruction phylogénétique
Le biais de la paralogie dans la reconstruction phylogénétique
Autres médias
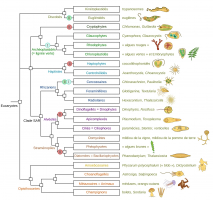
L’arbre montre les principaux groupes d’Eucaryotes (en termes de nombre d’espèces, d’importance écologique ou sanitaire). Les relations de parenté sont données d’après Keeling et Burki, 2019 1. Des exemples ainsi que des illustrations de membres des différents taxons sont donnés à droite. Les évène...
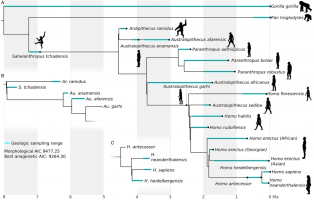
Cet arbre représente la meilleure estimation de Parins-Fukuchi et coll., 2018. À la différence d’autres méthodes de construction d’arbres phylogénétiques, n’utilisant que des données morphologiques, les auteurs estiment, dans l’étude dont est tirée cette figure, qu’il est préférable de recourir en p...
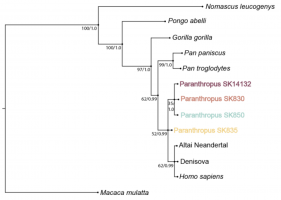
Les nombres aux nœuds représentent à gauche le bootstrap de 0 à 100 des réplicats de l’analyse par maximum de vraisemblance et à droite la probabilité à postériori de 0 à 1 de l’analyse par inférence bayésienne. Le bootstrap est une mesure permettant d’évaluer la stabilité d’un clade lorsque l’analy...
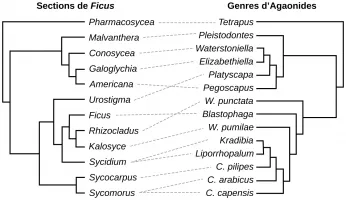
Le genre Ficus contient environ 800 espèces, ce qui en fait l’un des plus diversifiés de la flore tropicale. Les espèces y sont regroupées en sections, chaque section contenant quelques dizaines d’espèces : il y a par exemple la section Urostigma, la section Rhizocladus, etc. L’une des sections port...